Organismo modello
In questo articolo esploreremo a fondo l'argomento Organismo modello e tutti gli aspetti che lo circondano. Dalle sue origini ed evoluzione fino al suo impatto sulla società odierna, intraprenderemo un viaggio informativo che ci permetterà di comprendere meglio questo concetto. Attraverso ricerche, analisi e testimonianze cercheremo di far luce sugli aspetti più rilevanti di Organismo modello, offrendo una prospettiva ampia e completa. Allo stesso modo, esamineremo la sua rilevanza in diversi contesti e la sua influenza sulla vita quotidiana, fornendo al lettore una visione completa e arricchente. Preparatevi quindi ad immergervi nel mondo di Organismo modello e a scoprire tutto ciò che si nasconde dietro questo affascinante argomento.


Un organismo modello è una specie estensivamente studiata per comprendere particolari fenomeni biologici, in base al presupposto che le acquisizioni fatte sull'organismo modello possano fornire indicazioni sugli altri organismi. Ciò è possibile grazie al fatto che i principi biologici fondamentali, come le vie metaboliche, di regolazione e di sviluppo, e i geni che le codificano, si mantengono attraverso l'evoluzione.
Storicamente il primo organismo modello impiegato in esperimenti rigorosi per la comprensione dell'ereditarietà è stato il Pisum sativum di Gregor Mendel. Il pisello da orto infatti risponde a specifiche esigenze di incrocio controllato, rapido passo generazionale, prole numerosa, caratteri fenotipici alternativi e disponibilità di numerose varietà commerciali. Queste caratteristiche lo resero ottimale per un approccio ai problemi della ereditarietà di tipo quantitativo e statistico.
Criteri di scelta
Spesso, gli organismi modello vengono scelti in base alla loro capacità di essere adattabili a manipolazioni sperimentali. Di solito vengono preferite le seguenti caratteristiche: breve ciclo cellulare, tecniche per manipolazione genetica (ceppi inbred, linee di cellule staminali, e sistemi di transfezione). A volte, il riarrangiamento genetico favorisce il sequenziamento del genoma dell'organismo modello, per esempio, perché è molto compatto o per avere scarsa quantità di DNA non codificante, il cosiddetto "DNA spazzatura" (junk DNA).
Esistono numerosi organismi modello. Il primo organismo modello per la biologia molecolare probabilmente è stato il batterio E.coli, comunemente presente nel sistema digerente umano (e di solito ha attività benefica—il pericoloso ceppo Escherichia coli O157:H7 è raro). Viene utilizzato anche nello studio di molti batteriofagi, specialmente il fago lambda.
Negli eucarioti sono stati studiati approfonditamente alcuni lieviti, specialmente il Saccharomyces cerevisiae (lievito della birra), soprattutto perché sono facili da gestire. Il ciclo cellulare in un lievito è molto simile al ciclo cellulare negli umani ed è regolato da proteine omologhe. È stato studiato anche il moscerino della frutta Drosophila melanogaster, sempre perché è facile da gestire per essere un organismo multicellulare. Il verme Caenorhabditis elegans è stato studiato perché ha stadi di sviluppo estremamente definiti ed è possibile, quindi, rilevare rapidamente delle anormalità.
Quando i ricercatori cercano un organismo da usare nei loro studi, prendono in considerazione parecchie caratteristiche. Le più comuni sono le dimensioni, il tempo di generazione, l'accessibilità, la manipolazione, la genetica, la conservazione dei meccanismi e un potenziale beneficio economico. Con la diffusione della biologia molecolare comparata, i ricercatori hanno cercato organismi modello che rappresentassero diverse tipologie di vita.
Principali organismi modello
Virus
- Fago lambda è un batteriofago che infetta Escherichia coli
- Fago T4
- Fago Phi-X174 è stato il primo organismo sequenziato geneticamente.
- Virus del mosaico del tabacco
-
Placche di lisi di una coltura di E. coli da parte del batteriofago lambda.
-
Struttura del capside del batteriofago phi X 174
-
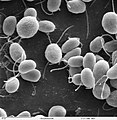
Microscopia elettronica del Virus del Mosaico del Tabacco TMV
-
Virus del Mosaico del Tabacco a 160 000 X ingrandimenti
Procarioti
- Escherichia coli è uno degli organismi unicellulari più studiati e più frequenti nell'intestino degli eucarioti superiori (ed in particolare di uccelli e mammiferi).
- Bacillus subtilis è un batterio del suolo, ampiamente studiato per la sua produzione di spore.
- Mycoplasma genitalium è un batterio parassita che vive nel tratto genitale e respiratorio dell'organismo umano.
- Vibrio fischeri è un organismo che vive in simbiosi con il calamaro delle Hawaii (Euprymna scolopes) ed è in grado di produrre la bioluminescenza necessaria al mollusco simbionte per illuminare l'ambiente circostante.
- Synechocystis è un cianobatterio ampiamente usato nello studio della fotosintesi.
- Pseudomonas fluorescens è un batterio del terreno in grado di diversificarsi velocemente in differenti linee cellulari.
-
Mappa genomica del M. genitalium
-
Capsula di Petri e Pseudomonas fluorescens
Eucarioti unicellulari
- Saccharomyces cerevisiae è noto come lievito della birra, è stato il primo eukaryota il cui genoma sia stato interamente sequenziato (nel 1996). Molto studiato per il suo ciclo cellulare.
- Schizosaccharomyces pombe è altro modello di lievito, che differisce da S. cerevisiae in particolare nella modalità di riproduzione: S. cerevisiae replica per gemmazione (budding), S. pombe per scissione binaria. Anche S.pombe è ampiamente studiato per il suo ciclo cellulare.
- Chlamydomonas reinhardtii è un'alga verde unicellulare, utilizzata per studiare fotosintesi, flagelli e motilità, regolazione del metabolismo, riconoscimento cellula-cellula, risposta all'affamamento e diversi altri processi biologici. Ha una genetica molto studiata, con una grande quantità di mutanti noti e sequenziati e procedure relativamente semplici per produrne di nuovi. La sua crescita in laboratorio è infatti semplice e poco costosa. Esiste un centro di raccolta delle informazioni genetiche su Chamydomonas presso la Università Duke negli Stati Uniti d'America.
- Tetrahymena thermophila è un protozoo ciliato di acqua dolce che presenta dimorfismo nucleare.
- Dictyostelium discoideum è specie appartenente al genere Dictyostelium, molto studiata come modello in biologia dello sviluppo, biologia molecolare nonché in tossicologia ambientale.
Eucarioti pluricellulari
Piante
- Arabidopsis thaliana è probabilmente la più importante pianta modello. Il suo studio ha fornito una considerevole quantità di nuove conoscenze. È una specie a crescita veloce. È stata la prima pianta il cui genoma sia stato interamente sequenziato. (Biologia molecolare, Citologia)
- Riso (Oryza sativa) è usato come modello per gli studi di biologia dei cereali. Il sequenziamento del suo genoma è in corso. (Agronomia, Biologia molecolare)
- Mais (Zea mais) è modello per lo studio dei cereali. Le sue caratteristiche genetiche hanno permesso lo sviluppo di teorie per la comprensione del ruolo dei trasposoni. Il suo genoma è stato sequenziato.
- Tobacco BY-2 cells è una linea cellulare coltivata in sospensione della pianta di tabacco (Nicotiana tabacum). Viene utilizzata per studi generali per studi fisiologici a livello di biologia cellulare delle piante. Il genoma di questa particolare cultivar non sarà sequenziato (non almeno nell'immediato futuro), mentre quello della specie selvatica, Nicotiana tabaccum è attualmente in corso.
- Lotus japonicus è usato come modello per le piante leguminose.
- Medicago truncatula è un altro modello per le leguminose. Il suo genoma, relativamente piccolo, è in sequenziamento.
- Brachypodium distachyon è un modello sperimentale emergente. Ha diversi attributi che lo rendono un eccellente modello per lo studio dei cereali.
- Lemna gibba è una pianta acquatica a rapida crescita, una delle più piccole piante da fiore. I tassi di crescita della Lemna sono utilizzati per valutare la tossicità dei prodotti chimici in ecotossicologia.
Funghi
- Aspergillus nidulans è un fungo filamentoso il cui genoma è stato interamente sequenziato.
- Neurospora crassa è una muffa aploide semplice da coltivare e nella quale è facile individuare fenotipi recessivi.
Invertebrati
- Arbacia punctulata è un riccio di mare della classe Echinoidea; è ancora ampiamente utilizzato come modello di embriogenesi.
- Caenorhabditis elegans è verme nematode, impiegato nello studio della differenziazione cellulare e dell'apoptosi.
- Cepaea nemoralis è un mollusco gasteropode utilizzato negli studi sulla ereditarietà e in biologia evolutiva.
- Ciona intestinalis è un'ascidia lunga, ottimo organismo modello per studi sul genoma: ha un numero limitato di geni (circa 15 000), un genoma compatto (circa 160 milioni di basi azotate) ed ha interessanti rapporti filogenetici con i vertebrati.
- Drosophila melanogaster è il moscerino della frutta, uno degli organismi viventi più studiati. È stato utilizzato, sin dai primi decenni del 1900, per studi di genetica di base. Oggi è considerato un ottimo modello animale per studi sul sistema nervoso e sul suo sviluppatissimo sistema visivo.
- Euprymna scolopes è il calamaro gigante delle Hawaii, modello di simbiosi tra animali e batteri (in particolare il Vibrio fischeri) nella produzione di sistemi bioluminescenti.
- Hydra è genere di organismi predatori di acqua dolce del phylum Cnidaria, dotati di simmetria radiale, molto studiati per l'alta capacità di rigenerazione.
- Loligo pealei è un calamaro, oggetto di ampi studi neurologici a causa del suo "assone gigante" (quasi 1 mm di diametro, circa 1 000 volte maggiore di un assone medio di mammifero).
- Paracentrotus lividus è un altro riccio di mare, anch'esso studiato da un punto di vista embriologico, ma anche da un punto di vista biomolecolare.
- Pristionchus pacificus è un verme cilindrico studiato nella biologia evolutiva dello sviluppo.
- Stomatogastric ganglion il cui sistema digestivo è modello per la genesi di pattern motori.
- Tribolium castaneum è il tribolio delle farine, un piccolo insetto che cresce agevolmente, studiato soprattutto in studi sul comportamento.
Vertebrati
- Brachydanio rerio o (Danio rerio) conosciuto come Pesce zebra, è un pesce d'acqua dolce molto usato negli acquari. Ha un corpo quasi trasparente durante il primo sviluppo, ciò fornisce un accesso visivo all'anatomia interna dell'animale. I Pesci zebra sono utilizzati per studiare lo sviluppo, la tossicologia e tossicopatologia e la specifica funzione del gene e il ruolo delle vie di segnalazione.
- Canis lupus familiaris è importante modello dei sistemi respiratorio e cardiovascolare.
- Cavia porcellus porcellino d'India, detto comunemente cavia, è la cavia, usata inizialmente da Robert Koch e altri batteriologi, è diventata nella lingua italiana l'"animale di laboratorio" per antonomasia, sebbene oggigiorno non sia più molto usata dai ricercatori.
- Coturnix coturnix è nota come quaglia e viene utilizzata in esperimenti di embriologia perché presenta cellule colorate che permettono di utilizzarle in esperimenti di trapianto sul pollo.
- Cricetinae è noto come Criceto ed è usato nelle ricerche sulla leishmaniosi.
- Felis sylvestris catus è il gatto ed è usato nelle ricerche di neurofisiologia.
- Gallus gallus è il pollo, ed è particolarmente impiegato negli studi sullo sviluppo embrionale, in quanto facilmente maneggiabile e a rapido sviluppo.
- Macaca mulatta è il Rhesus macaque o macaco e viene usato negli studi sulla cognizione e nelle malattie infettive.
- Mus musculus è il topo, il modello animale più utilizzato nella ricerca biomedica. Ne esistono numerose linee inbred: alcune sono state selezionate per mostrare particolari tratti, spesso di interesse medico, come il peso corporeo, la muscolatura, l'obesità.
- Oryzias latipes è un altro pesce, noto come medaka. Utilizzato anch'esso come modello di sviluppo, soprattutto dell'occhio, ha il vantaggio di essere più resistente del Pesce zebra.
- Rattus norvegicus è il ratto, ampiamente usato come modello animale in tossicologia; molto utile come modello neurologico e come fonte di colture primarie.
- Sigmodon hispidus è usato nelle ricerche sulla poliomielite.
- Sus domesticus è il maiale, ed è il modello animale utilizzato negli studi pre-clinici di patologie come le retinopatie. Una probabile applicazione futura è quella di modello per gene therapy.
- Taeniopygia guttata (Zebra finch) o diamante mandarino viene usato per studi sugli apparati uditivi dei non mammiferi.
- Takifugu rubipres è noto come pesce palla, ha un genoma molto compatto, con poco junk DNA.
- Xenopus laevis è un rospo africano, anch'esso molto usato in studi di biologia evolutiva dello sviluppo, soprattutto a causa delle dimensioni ampie delle sue cellule uovo.
Organismi modello usati per specifiche ricerche
Selezione e conflitti sessuali
- Callosobruchus maculatus
- Chorthippus parallelus
- Coelopidae
- Diopsidae
- Drosophila spp.
- Macrostomum lignano
- Gryllus bimaculatus
- Scathophaga stercoraria
Zone ibride
- Bombina spp.
- Podisma spp.
- Caledia captiva (Orthoptera)
Ecologia genomica
- Daphnia pulex, un organismo modello di indicatore comportamentale.
Tavola genetica degli organismi modello
La tabella indica lo status del Progetto genoma per ciascun organismo, mostrando dell'organismo la ricombinazione omologa e lo stato delle conoscenze delle vie biochimiche dell'organismo.
| Organismo | Sequenziamento del genoma | Ricombinazione omologa | Biochimica |
|---|---|---|---|
| Procariota | |||
| Escherichia coli | Si | Si | Eccellente |
| Eucariota unicellulare | |||
| Dictyostelium discoideum | Si | Si | Eccellente |
| Saccharomyces cerevisiae | Si | Si | Buono |
| Schizosaccharomyces pombe | Si | Si | Buono |
| Chlamydomonas reinhardtii | Si | No | Buono |
| Tetrahymena thermophila | Si | Si | Buono |
| Eucariota pluricellulare | |||
| Caenorhabditis elegans | Si | Difficoltoso | Non così buono |
| Drosophila melanogaster | Si | Difficile | Buono |
| Arabidopsis thaliana | Si | No | Cattivo |
| Physcomitrella patens | Si | Si | Eccellente |
| Vertebrato | |||
| Danio rerio | Si | No | Buono |
| Mus musculus | Si | Si | Buono |
| Xenopus laevis | Si | ||
| Homo sapiens NB: non è un organismo modello | Si | Si | Buono |
Note
- ^ JL. Weller, V. Hecht, LC. Liew, FC. Sussmilch, B. Wenden, CL. Knowles, Vander Schoor, Update on the genetic control of flowering in garden pea., in J Exp Bot, vol. 60, n. 9, 2009, pp. 2493-9, DOI:10.1093/jxb/erp120, PMID 19414500.
- ^ M. Bhattacharyya, C. Martin e A. Smith, The importance of starch biosynthesis in the wrinkled seed shape character of peas studied by Mendel., in Plant Mol Biol, vol. 22, n. 3, giugno 1993, pp. 525-31, PMID 8329688.
- ^ WW. Piegorsch, RA. Fisher, JG. Mendel, Fisher's contributions to genetics and heredity, with special emphasis on the Gregor Mendel controversy., in Biometrics, vol. 46, n. 4, dicembre 1990, pp. 915-24, PMID 2085640.
- ^ G. Wegrzyn e A. Wegrzyn, , in Postepy Biochem, vol. 52, n. 1, 2006, pp. 42-8, PMID 16869300.
- ^ SN. Austad, Methusaleh's Zoo: how nature provides us with clues for extending human health span., in J Comp Pathol, 142 Suppl 1, gennaio 2010, pp. S10-21, DOI:10.1016/j.jcpa.2009.10.024, PMID 19962715.
- ^ AW. Briggs, U. Stenzel, PL. Johnson, RE. Green, J. Kelso, K. Prüfer, M. Meyer, J. Krause e MT. Ronan, Patterns of damage in genomic DNA sequences from a Neandertal., in Proc Natl Acad Sci U S A, vol. 104, n. 37, settembre 2007, pp. 14616-21, DOI:10.1073/pnas.0704665104, PMID 17715061.
- ^ O. Tenaillon, OK. Silander, JP. Uzan e L. Chao, Quantifying organismal complexity using a population genetic approach., in PLoS One, vol. 2, n. 2, 2007, pp. e217, DOI:10.1371/journal.pone.0000217, PMID 17299597.
- ^ JS. Lim, SM. Kim, SY. Lee, EA. Stach, JN. Culver e MT. Harris, Quantitative study of Au(III) and Pd(II) ion biosorption on genetically engineered Tobacco mosaic virus., in J Colloid Interface Sci, vol. 342, n. 2, febbraio 2010, pp. 455-61, DOI:10.1016/j.jcis.2009.10.028, PMID 19914631.
- ^ J. Lewis, From virus research to molecular biology: Tobacco mosaic virus in Germany, 1936-1956., in J Hist Biol, vol. 37, n. 2, 2004, pp. 259-301, PMID 15490522.
- ^ G. Stahl, L. Bidou, JP. Rousset e M. Cassan, Versatile vectors to study recoding: conservation of rules between yeast and mammalian cells., in Nucleic Acids Res., vol. 23, n. 9, maggio 1995, pp. 1557-60, PMID 7784210.
- ^ NS. Persky e ST. Lovett, Mechanisms of recombination: lessons from E. coli., in Crit Rev Biochem Mol Biol, vol. 43, n. 6, pp. 347-70, DOI:10.1080/10409230802485358, PMID 19016098.
- ^ C. Kaleta, A. Göhler, S. Schuster, K. Jahreis, R. Guthke e S. Nikolajewa, Integrative inference of gene-regulatory networks in Escherichia coli using information theoretic concepts and sequence analysis., in BMC Syst Biol, vol. 4, 2010, p. 116, DOI:10.1186/1752-0509-4-116, PMID 20718955.
- ^ J. Bohlin e E. Skjerve, Examination of genome homogeneity in prokaryotes using genomic signatures., in PLoS One, vol. 4, n. 12, 2009, pp. e8113, DOI:10.1371/journal.pone.0008113, PMID 19956556.
- ^ EB. Johnston, PJ. Lewis e R. Griffith, The interaction of Bacillus subtilis sigmaA with RNA polymerase., in Protein Sci, vol. 18, n. 11, novembre 2009, pp. 2287-97, DOI:10.1002/pro.239, PMID 19735077.
- ^ CD. Vázquez, JA. Freyre-González, G. Gosset, JA. Loza e RM. Gutiérrez-Ríos, Identification of network topological units coordinating the global expression response to glucose in Bacillus subtilis and its comparison to Escherichia coli., in BMC Microbiol, vol. 9, 2009, p. 176, DOI:10.1186/1471-2180-9-176, PMID 19703276.
- ^ A. Srivatsan, Y. Han, J. Peng, AK. Tehranchi, R. Gibbs, JD. Wang e R. Chen, High-precision, whole-genome sequencing of laboratory strains facilitates genetic studies., in PLoS Genet, vol. 4, n. 8, 2008, pp. e1000139, DOI:10.1371/journal.pgen.1000139, PMID 18670626.
- ^ A. Barré, A. de Daruvar e A. Blanchard, MolliGen, a database dedicated to the comparative genomics of Mollicutes., in Nucleic Acids Res, vol. 32, Database issue, gennaio 2004, pp. D307-10, DOI:10.1093/nar/gkh114, PMID 14681420.
- ^ H. Bang, A. Pecht, G. Raddatz, T. Scior, W. Solbach, K. Brune e A. Pahl, Prolyl isomerases in a minimal cell. Catalysis of protein folding by trigger factor from Mycoplasma genitalium., in Eur J Biochem, vol. 267, n. 11, giugno 2000, pp. 3270-80, PMID 10824113.
- ^ AR. Mushegian e EV. Koonin, A minimal gene set for cellular life derived by comparison of complete bacterial genomes., in Proc Natl Acad Sci U S A, vol. 93, n. 19, settembre 1996, pp. 10268-73, PMID 8816789.
- ^ a b AK. Dunn e EV. Stabb, Genetic analysis of trimethylamine N-oxide reductases in the light organ symbiont Vibrio fischeri ES114., in J Bacteriol, vol. 190, n. 17, settembre 2008, pp. 5814-23, DOI:10.1128/JB.00227-08, PMID 18606737.
- ^ EA. Meighen, Bacterial bioluminescence: organization, regulation, and application of the lux genes., in FASEB J, vol. 7, n. 11, agosto 1993, pp. 1016-22, PMID 8370470.
- ^ M. Nakao, S. Okamoto, M. Kohara, T. Fujishiro, T. Fujisawa, S. Sato, S. Tabata, T. Kaneko e Y. Nakamura, CyanoBase: the cyanobacteria genome database update 2010., in Nucleic Acids Res, vol. 38, Database issue, gennaio 2010, pp. D379-81, DOI:10.1093/nar/gkp915, PMID 19880388.
- ^ SY. Gerdes, OV. Kurnasov, K. Shatalin, B. Polanuyer, R. Sloutsky, V. Vonstein, R. Overbeek e AL. Osterman, Comparative genomics of NAD biosynthesis in cyanobacteria., in J Bacteriol, vol. 188, n. 8, aprile 2006, pp. 3012-23, DOI:10.1128/JB.188.8.3012-3023.2006, PMID 16585762.
- ^ M. Zanetti, E. Teardo, N. La Rocca, L. Zulkifli, V. Checchetto, T. Shijuku, Y. Sato, GM. Giacometti e N. Uozumi, A novel potassium channel in photosynthetic cyanobacteria., in PLoS One, vol. 5, n. 4, 2010, pp. e10118, DOI:10.1371/journal.pone.0010118, PMID 20404935.
- ^ HJ. Eberl e S. Collinson, A modeling and simulation study of siderophore mediated antagonism in dual-species biofilms., in Theor Biol Med Model, vol. 6, 2009, p. 30, DOI:10.1186/1742-4682-6-30, PMID 20028518.
- ^ VO. Stockwell e JP. Stack, Using Pseudomonas spp. for Integrated Biological Control., in Phytopathology, vol. 97, n. 2, febbraio 2007, pp. 244-9, DOI:10.1094/PHYTO-97-2-0244, PMID 18944382.
- ^ LE. Jensen e O. Nybroe, Nitrogen availability to Pseudomonas fluorescens DF57 is limited during decomposition of barley straw in bulk soil and in the barley rhizosphere., in Appl Environ Microbiol, vol. 65, n. 10, ottobre 1999, pp. 4320-8, PMID 10508054.
- ^ a b c C. Stark, BJ. Breitkreutz, A. Chatr-Aryamontri, L. Boucher, R. Oughtred, MS. Livstone, J. Nixon, K. Van Auken e X. Wang, The BioGRID Interaction Database: 2011 update., in Nucleic Acids Res, novembre 2010, DOI:10.1093/nar/gkq1116, PMID 21071413.
- ^ SR. Birkeland, N. Jin, AC. Ozdemir, RH. Lyons, LS. Weisman e TE. Wilson, Discovery of Mutations in Saccharomyces cerevisiae by Pooled Linkage Analysis and Whole Genome Sequencing., in Genetics, ottobre 2010, DOI:10.1534/genetics.110.123232, PMID 20923977.
- ^ S. Bordel, R. Agren e J. Nielsen, Sampling the solution space in genome-scale metabolic networks reveals transcriptional regulation in key enzymes., in PLoS Comput Biol, vol. 6, n. 7, 2010, pp. e1000859, DOI:10.1371/journal.pcbi.1000859, PMID 20657658.
- ^ A. Goffeau, BG. Barrell, H. Bussey, RW. Davis, B. Dujon, H. Feldmann, F. Galibert, JD. Hoheisel e C. Jacq, Life with 6000 genes., in Science, vol. 274, n. 5287, ottobre 1996, pp. 546, 563-7, PMID 8849441.
- ^ D. Dardalhon, AR. Angelin, G. Baldacci, E. Sage e S. Francesconi, Unconventional effects of UVA radiation on cell cycle progression in S. pombe., in Cell Cycle, vol. 7, n. 5, marzo 2008, pp. 611-22, PMID 18256544.
- ^ CJ. Webb e VA. Zakian, Identification and characterization of the Schizosaccharomyces pombe TER1 telomerase RNA., in Nat Struct Mol Biol, vol. 15, n. 1, gennaio 2008, pp. 34-42, DOI:10.1038/nsmb1354, PMID 18157149.
- ^ H. Lin, AL. Kwan e SK. Dutcher, Synthesizing and salvaging NAD: lessons learned from Chlamydomonas reinhardtii., in PLoS Genet, vol. 6, n. 9, 2010, DOI:10.1371/journal.pgen.1001105, PMID 20838591.
- ^ S. Shaver, JA. Casas-Mollano, RL. Cerny e H. Cerutti, Origin of the polycomb repressive complex 2 and gene silencing by an E(z) homolog in the unicellular alga Chlamydomonas., in Epigenetics, vol. 5, n. 4, maggio 2010, pp. 301-12, PMID 20421736.
- ^ G. Periz, D. Dharia, SH. Miller e LR. Keller, Flagellar elongation and gene expression in Chlamydomonas reinhardtii., in Eukaryot Cell, vol. 6, n. 8, agosto 2007, pp. 1411-20, DOI:10.1128/EC.00167-07, PMID 17573545.
- ^ PH. Brito, E. Guilherme, H. Soares e I. Gordo, Mutation accumulation in Tetrahymena., in BMC Evol Biol, vol. 10, n. 1, novembre 2010, p. 354, DOI:10.1186/1471-2148-10-354, PMID 21078144.
- ^ BP. Culver, JB. Meehl, TH. Giddings e M. Winey, The two SAS-6 homologs in Tetrahymena thermophila have distinct functions in basal body assembly., in Mol Biol Cell, vol. 20, n. 6, marzo 2009, pp. 1865-77, DOI:10.1091/mbc.E08-08-0838, PMID 19158390.
- ^ JA. Eisen, RS. Coyne, M. Wu, D. Wu, M. Thiagarajan, JR. Wortman, JH. Badger, Q. Ren e P. Amedeo, Macronuclear genome sequence of the ciliate Tetrahymena thermophila, a model eukaryote., in PLoS Biol, vol. 4, n. 9, settembre 2006, pp. e286, DOI:10.1371/journal.pbio.0040286, PMID 16933976.
- ^ G. Glöckner e AJ. Heidel, Centromere sequence and dynamics in Dictyostelium discoideum., in Nucleic Acids Res, vol. 37, n. 6, aprile 2009, pp. 1809-16, DOI:10.1093/nar/gkp017, PMID 19179372.
- ^ JM. Joseph, P. Fey, N. Ramalingam, XI. Liu, M. Rohlfs, AA. Noegel, A. Müller-Taubenberger, G. Glöckner e M. Schleicher, The actinome of Dictyostelium discoideum in comparison to actins and actin-related proteins from other organisms., in PLoS One, vol. 3, n. 7, 2008, pp. e2654, DOI:10.1371/journal.pone.0002654, PMID 18612387.
- ^ A. Sillo, G. Bloomfield, A. Balest, A. Balbo, B. Pergolizzi, B. Peracino, J. Skelton, A. Ivens e S. Bozzaro, Genome-wide transcriptional changes induced by phagocytosis or growth on bacteria in Dictyostelium., in BMC Genomics, vol. 9, 2008, p. 291, DOI:10.1186/1471-2164-9-291, PMID 18559084.
- ^ a b JX. Yue, J. Li, D. Wang, H. Araki, D. Tian e S. Yang, Genome-wide investigation reveals high evolutionary rates in annual model plants., in BMC Plant Biol, vol. 10, n. 1, novembre 2010, p. 242, DOI:10.1186/1471-2229-10-242, PMID 21062446.
- ^ E. Wywial e SM. Singh, Identification and structural characterization of FYVE domain-containing proteins of Arabidopsis thaliana., in BMC Plant Biol, vol. 10, 2010, p. 157, DOI:10.1186/1471-2229-10-157, PMID 20678208.
- ^ J. Kane, M. Freeling e E. Lyons, The evolution of a high copy gene array in Arabidopsis., in J Mol Evol, vol. 70, n. 6, giugno 2010, pp. 531-44, DOI:10.1007/s00239-010-9350-2, PMID 20495794.
- ^ JE. Bowers, MA. Arias, R. Asher, JA. Avise, RT. Ball, GA. Brewer, RW. Buss, AH. Chen e TM. Edwards, Comparative physical mapping links conservation of microsynteny to chromosome structure and recombination in grasses., in Proc Natl Acad Sci U S A, vol. 102, n. 37, settembre 2005, pp. 13206-11, DOI:10.1073/pnas.0502365102, PMID 16141333.
- ^ CE. Gallagher, PD. Matthews, F. Li e ET. Wurtzel, Gene duplication in the carotenoid biosynthetic pathway preceded evolution of the grasses., in Plant Physiol., vol. 135, n. 3, luglio 2004, pp. 1776-83, DOI:10.1104/pp.104.039818, PMID 15247400.
- ^ H. Lin, S. Ouyang, A. Egan, K. Nobuta, BJ. Haas, W. Zhu, X. Gu, JC. Silva e BC. Meyers, Characterization of paralogous protein families in rice., in BMC Plant Biol, vol. 8, 2008, p. 18, DOI:10.1186/1471-2229-8-18, PMID 18284697.
- ^ S. Fu, R. Meeley e MJ. Scanlon, Empty pericarp2 encodes a negative regulator of the heat shock response and is required for maize embryogenesis., in Plant Cell, vol. 14, n. 12, dicembre 2002, pp. 3119-32, PMID 12468731.
- ^ DR. Kovar, BK. Drøbak, DA. Collings e CJ. Staiger, The characterization of ligand-specific maize (Zea mays) profilin mutants., in Biochem J, vol. 358, Pt 1, agosto 2001, pp. 49-57, PMID 11485551.
- ^ M. Deutsch e M. Long, Intron-exon structures of eukaryotic model organisms., in Nucleic Acids Res, vol. 27, n. 15, agosto 1999, pp. 3219-28, PMID 10454621.
- ^ M. Langer, LF. Sniderhan, U. Grossniklaus e A. Ray, Transposon excision from an atypical site: a mechanism of evolution of novel transposable elements., in PLoS One, vol. 2, n. 10, 2007, pp. e965, DOI:10.1371/journal.pone.0000965, PMID 17912344.
- ^ AM. Jovanović, S. Durst e P. Nick, Plant cell division is specifically affected by nitrotyrosine., in J Exp Bot, vol. 61, n. 3, marzo 2010, pp. 901-9, DOI:10.1093/jxb/erp369, PMID 20018903.
- ^ K. Eggenberger, E. Birtalan, T. Schröder, S. Bräse e P. Nick, Passage of Trojan peptoids into plant cells., in Chembiochem, vol. 10, n. 15, ottobre 2009, pp. 2504-12, DOI:10.1002/cbic.200900331, PMID 19739189.
- ^ K. Szczyglowski e J. Stougaard, Lotus genome: pod of gold for legume research., in Trends Plant Sci, vol. 13, n. 10, ottobre 2008, pp. 515-7, DOI:10.1016/j.tplants.2008.08.001, PMID 18762442.
- ^ J. Ramos, L. Naya, M. Gay, J. Abián e M. Becana, Functional characterization of an unusual phytochelatin synthase, LjPCS3, of Lotus japonicus., in Plant Physiol, vol. 148, n. 1, settembre 2008, pp. 536-45, DOI:10.1104/pp.108.121715, PMID 18614711.
- ^ F. Alkhalfioui, M. Renard, WH. Vensel, J. Wong, CK. Tanaka, WJ. Hurkman, BB. Buchanan e F. Montrichard, Thioredoxin-linked proteins are reduced during germination of Medicago truncatula seeds., in Plant Physiol, vol. 144, n. 3, luglio 2007, pp. 1559-79, DOI:10.1104/pp.107.098103, PMID 17513483.
- ^ AF. Lamblin, JA. Crow, JE. Johnson, KA. Silverstein, TM. Kunau, A. Kilian, D. Benz, M. Stromvik e G. Endré, MtDB: a database for personalized data mining of the model legume Medicago truncatula transcriptome., in Nucleic Acids Res, vol. 31, n. 1, gennaio 2003, pp. 196-201, PMID 12519981.
- ^ L. Tyler, JN. Bragg, J. Wu, X. Yang, GA. Tuskan e JP. Vogel, Annotation and comparative analysis of the glycoside hydrolase genes in Brachypodium distachyon., in BMC Genomics, vol. 11, 2010, p. 600, DOI:10.1186/1471-2164-11-600, PMID 20973991.
- ^ T. Unver e H. Budak, Conserved microRNAs and their targets in model grass species Brachypodium distachyon., in Planta, vol. 230, n. 4, settembre 2009, pp. 659-69, DOI:10.1007/s00425-009-0974-7, PMID 19585143.
- ^ EB. McGregor, KR. Solomon e ML. Hanson, Monensin is not toxic to aquatic macrophytes at environmentally relevant concentrations., in Arch Environ Contam Toxicol, vol. 53, n. 4, novembre 2007, pp. 541-51, DOI:10.1007/s00244-007-0002-5, PMID 17657449.
- ^ S. Shrivastava, R. Poddar, P. Shukla e K. Mukhopadhyay, Study of codon bias perspective of fungal xylanase gene by multivariate analysis., in Bioinformation, vol. 3, n. 10, 2009, pp. 425-9, PMID 19759864.
- ^ I. Sato, M. Shimizu, T. Hoshino e N. Takaya, The glutathione system of Aspergillus nidulans involves a fungus-specific glutathione S-transferase., in J Biol Chem, vol. 284, n. 12, marzo 2009, pp. 8042-53, DOI:10.1074/jbc.M807771200, PMID 19171936.
- ^ G. Panagiotou, MR. Andersen, T. Grotkjaer, TB. Regueira, G. Hofmann, J. Nielsen e L. Olsson, Systems analysis unfolds the relationship between the phosphoketolase pathway and growth in Aspergillus nidulans., in PLoS One, vol. 3, n. 12, 2008, pp. e3847, DOI:10.1371/journal.pone.0003847, PMID 19052639.
- ^ C. Tian, WT. Beeson, AT. Iavarone, J. Sun, MA. Marletta, JH. Cate e NL. Glass, Systems analysis of plant cell wall degradation by the model filamentous fungus Neurospora crassa., in Proc Natl Acad Sci U S A, vol. 106, n. 52, dicembre 2009, pp. 22157-62, DOI:10.1073/pnas.0906810106, PMID 20018766.
- ^ N. Liu, ZD. Xiao, CH. Yu, P. Shao, YT. Liang, DG. Guan, JH. Yang, CL. Chen e LH. Qu, SnoRNAs from the filamentous fungus Neurospora crassa: structural, functional and evolutionary insights., in BMC Genomics, vol. 10, 2009, p. 515, DOI:10.1186/1471-2164-10-515, PMID 19895704.
- ^ NB. Raju, Neurospora as a model fungus for studies in cytogenetics and sexual biology at Stanford., in J Biosci, vol. 34, n. 1, marzo 2009, pp. 139-59, PMID 19430125.
- ^ DE. Heck, L. Louis, MA. Gallo e JD. Laskin, Modulation of the development of plutei by nitric oxide in the sea urchin Arbacia punctulata., in Biol Bull, vol. 199, n. 2, ottobre 2000, pp. 195-7, PMID 11081732.
- ^ DE. Heck e JD. Laskin, Ryanodine-sensitive calcium flux regulates motility of Arbacia punctulata sperm., in Biol Bull, vol. 205, n. 2, ottobre 2003, pp. 185-6, PMID 14583520.
- ^ MN. Semenova e ND. Ozerniuk, , in Zh Evol Biokhim Fiziol, vol. 40, n. 3, pp. 229-34, PMID 15453454.
- ^ WA. Anderson e ME. Perotti, An ultracytochemical study of the respiratory potency, integrity, and fate of the sea urchin sperm mitochondria during early embryogenesis., in J. Cell. Biol., vol. 66, n. 2, agosto 1975, pp. 367-76, DOI:10.1083/jcb.66.2.367, PMID 167033.
- ^ JM. Noronha, GH. Sheys e JM. Buchanan, Induction of a reductive pathway for deoxyribonucleotide synthesis during early embryogenesis of the sea urchin., in Proc Natl Acad Sci U S A, vol. 69, n. 8, agosto 1972, pp. 2006-10, PMID 4626400.
- ^ M. Doitsidou, RJ. Poole, S. Sarin, H. Bigelow e O. Hobert, C. elegans Mutant Identification with a One-Step Whole-Genome-Sequencing and SNP Mapping Strategy., in PLoS One, vol. 5, n. 11, 2010, pp. e15435, DOI:10.1371/journal.pone.0015435, PMID 21079745.
- ^ O. Hobert, Neurogenesis in the nematode Caenorhabditis elegans., in WormBook, 2010, pp. 1-24, DOI:10.1895/wormbook.1.12.2, PMID 20891032.
- ^ H. Furuhashi, T. Takasaki, A. Rechtsteiner, T. Li, H. Kimura, PM. Checchi, S. Strome e WG. Kelly, Trans-generational epigenetic regulation of C. elegans primordial germ cells., in Epigenetics Chromatin, vol. 3, n. 1, 2010, p. 15, DOI:10.1186/1756-8935-3-15, PMID 20704745.
- ^ N. Noren Hooten, K. Abdelmohsen, M. Gorospe, N. Ejiogu, AB. Zonderman e MK. Evans, microRNA expression patterns reveal differential expression of target genes with age., in PLoS One, vol. 5, n. 5, 2010, pp. e10724, DOI:10.1371/journal.pone.0010724, PMID 20505758.
- ^ A. Viñuela, LB. Snoek, JA. Riksen e JE. Kammenga, Genome-wide gene expression regulation as a function of genotype and age in C. elegans., in Genome Res, vol. 20, n. 7, luglio 2010, pp. 929-37, DOI:10.1101/gr.102160.109, PMID 20488933.
- ^ HE. Arda, S. Taubert, LT. MacNeil, CC. Conine, B. Tsuda, M. Van Gilst, R. Sequerra, L. Doucette-Stamm e KR. Yamamoto, Functional modularity of nuclear hormone receptors in a Caenorhabditis elegans metabolic gene regulatory network., in Mol Syst Biol, vol. 6, maggio 2010, p. 367, DOI:10.1038/msb.2010.23, PMID 20461074.
- ^ CC. Yang, YT. Wang, YY. Hsiao, LG. Doudeva, PH. Kuo, SY. Chow e HS. Yuan, Structural and biochemical characterization of CRN-5 and Rrp46: an exosome component participating in apoptotic DNA degradation., in RNA, vol. 16, n. 9, settembre 2010, pp. 1748-59, DOI:10.1261/rna.2180810, PMID 20660080.
- ^ X. Teng e JM. Hardwick, The apoptosome at high resolution., in Cell, vol. 141, n. 3, aprile 2010, pp. 402-4, DOI:10.1016/j.cell.2010.04.015, PMID 20434981.
- ^ T. Sakashita, T. Takanami, S. Yanase, N. Hamada, M. Suzuki, T. Kimura, Y. Kobayashi, N. Ishii e A. Higashitani, Radiation biology of Caenorhabditis elegans: germ cell response, aging and behavior., in J Radiat Res (Tokyo), vol. 51, n. 2, marzo 2010, pp. 107-21, PMID 20208402.
- ^ LM. Cook, Disequilibrium in some Cepaea populations., in Heredity, vol. 94, n. 5, maggio 2005, pp. 497-500, DOI:10.1038/sj.hdy.6800645, PMID 15742002.
- ^ A. Davison e B. Clarke, History or current selection? A molecular analysis of 'area effects' in the land snail Cepaea nemoralis., in Proc Biol Sci, vol. 267, n. 1451, luglio 2000, pp. 1399-405, DOI:10.1098/rspb.2000.1156, PMID 10983823.
- ^ A. Bellido, L. Madec, JF. Arnaud e A. Guiller, Spatial structure of shell polychromatism in populations of Cepaea nemoralis: new techniques for an old debate., in Heredity, vol. 88, n. 1, gennaio 2002, pp. 75-82, DOI:10.1038/sj.hdy.6800012, PMID 11813110.
- ^ L. Christiaen, B. Davidson, T. Kawashima, W. Powell, H. Nolla, K. Vranizan e M. Levine, The transcription/migration interface in heart precursors of Ciona intestinalis., in Science, vol. 320, n. 5881, giugno 2008, pp. 1349-52, DOI:10.1126/science.1158170, PMID 18535245.
- ^ H. Auger, C. Lamy, M. Haeussler, P. Khoueiry, P. Lemaire e JS. Joly, Similar regulatory logic in Ciona intestinalis for two Wnt pathway modulators, ROR and SFRP-1/5., in Dev Biol, vol. 329, n. 2, maggio 2009, pp. 364-73, DOI:10.1016/j.ydbio.2009.02.018, PMID 19248777.
- ^ A. Nakayama-Ishimura, JP. Chambon, T. Horie, N. Satoh e Y. Sasakura, Delineating metamorphic pathways in the ascidian Ciona intestinalis., in Dev Biol, vol. 326, n. 2, febbraio 2009, pp. 357-67, DOI:10.1016/j.ydbio.2008.11.026, PMID 19100250.
- ^ MT. Yamamoto, Drosophila Genetic Resource and Stock Center; The National BioResource Project., in Exp Anim, vol. 59, n. 2, 2010, pp. 125-38, PMID 20484846.
- ^ JC. Tuthill, Lessons from a compartmental model of a Drosophila neuron., in J Neurosci, vol. 29, n. 39, settembre 2009, pp. 12033-4, DOI:10.1523/JNEUROSCI.3348-09.2009, PMID 19793961.
- ^ J. Pearson, L. López-Onieva, P. Rojas-Ríos e A. González-Reyes, Recent advances in Drosophila stem cell biology., in Int J Dev Biol, vol. 53, n. 8-10, 2009, pp. 1329-39, DOI:10.1387/ijdb.072431jp, PMID 19247935.
- ^ AD. Huberman, TR. Clandinin e H. Baier, Molecular and cellular mechanisms of lamina-specific axon targeting., in Cold Spring Harb Perspect Biol, vol. 2, n. 3, marzo 2010, pp. a001743, DOI:10.1101/cshperspect.a001743, PMID 20300211.
- ^ S. Broughton e L. Partridge, Insulin/IGF-like signalling, the central nervous system and aging., in Biochem J, vol. 418, n. 1, febbraio 2009, pp. 1-12, DOI:10.1042/BJ20082102, PMID 19159343.
- ^ N. Hafer e P. Schedl, Dissection of larval CNS in Drosophila melanogaster., in J Vis Exp, n. 1, dicembre 2006, p. 85, DOI:10.3791/85, PMID 18704179.
- ^ CK. Beam e K. Moberg, The gang of four gene regulates growth and patterning of the developing Drosophila eye., in Fly (Austin), vol. 4, n. 2, aprile 2010, pp. 104-16, PMID 20473027.
- ^ Y. Zhan, NY. Melian, M. Pantoja, N. Haines, H. Ruohola-Baker, CW. Bourque, Y. Rao e S. Carbonetto, Dystroglycan and mitochondrial ribosomal protein l34 regulate differentiation in the Drosophila eye., in PLoS One, vol. 5, n. 5, 2010, pp. e10488, DOI:10.1371/journal.pone.0010488, PMID 20463973.
- ^ LC. Firth, A. Bhattacharya e NE. Baker, Cell cycle arrest by a gradient of Dpp signaling during Drosophila eye development., in BMC Dev Biol, vol. 10, 2010, p. 28, DOI:10.1186/1471-213X-10-28, PMID 20214806.
- ^ MS. Wollenberg e EG. Ruby, Population structure of Vibrio fischeri within the light organs of Euprymna scolopes squid from Two Oahu (Hawaii) populations., in Appl Environ Microbiol, vol. 75, n. 1, gennaio 2009, pp. 193-202, DOI:10.1128/AEM.01792-08, PMID 18997024.
- ^ Y. Wang, YS. Dufour, HK. Carlson, TJ. Donohue, MA. Marletta e EG. Ruby, H-NOX-mediated nitric oxide sensing modulates symbiotic colonization by Vibrio fischeri., in Proc Natl Acad Sci U S A, vol. 107, n. 18, maggio 2010, pp. 8375-80, DOI:10.1073/pnas.1003571107, PMID 20404170.
- ^ AM. Wier, SV. Nyholm, MJ. Mandel, RP. Massengo-Tiassé, AL. Schaefer, I. Koroleva, S. Splinter-Bondurant, B. Brown e L. Manzella, Transcriptional patterns in both host and bacterium underlie a daily rhythm of anatomical and metabolic change in a beneficial symbiosis., in Proc Natl Acad Sci U S A, vol. 107, n. 5, febbraio 2010, pp. 2259-64, DOI:10.1073/pnas.0909712107, PMID 20133870.
- ^ D. Tong, NS. Rozas, TH. Oakley, J. Mitchell, NJ. Colley e MJ. McFall-Ngai, Evidence for light perception in a bioluminescent organ., in Proc Natl Acad Sci U S A, vol. 106, n. 24, giugno 2009, pp. 9836-41, DOI:10.1073/pnas.0904571106, PMID 19509343.
- ^ HR. Bode, Axial patterning in hydra., in Cold Spring Harb Perspect Biol, vol. 1, n. 1, luglio 2009, pp. a000463, DOI:10.1101/cshperspect.a000463, PMID 20066073.
- ^ RE. Steele e CE. Dana, Evolutionary history of the HAP2/GCS1 gene and sexual reproduction in metazoans., in PLoS One, vol. 4, n. 11, 2009, pp. e7680, DOI:10.1371/journal.pone.0007680, PMID 19888453.
- ^ K. Khalturin, F. Anton-Erxleben, S. Sassmann, J. Wittlieb, G. Hemmrich e TC. Bosch, A novel gene family controls species-specific morphological traits in Hydra., in PLoS Biol, vol. 6, n. 11, novembre 2008, pp. e278, DOI:10.1371/journal.pbio.0060278, PMID 19018660.
- ^ H. Meinhardt, Models for the generation and interpretation of gradients., in Cold Spring Harb Perspect Biol, vol. 1, n. 4, ottobre 2009, pp. a001362, DOI:10.1101/cshperspect.a001362, PMID 20066097.
- ^ T. Fujisawa, Hydra regeneration and epitheliopeptides., in Dev Dyn, vol. 226, n. 2, febbraio 2003, pp. 182-9, DOI:10.1002/dvdy.10221, PMID 12557197.
- ^ KM. Smith, L. Gee e HR. Bode, HyAlx, an aristaless-related gene, is involved in tentacle formation in hydra., in Development, vol. 127, n. 22, novembre 2000, pp. 4743-52, PMID 11044390.
- ^ P. Grant, Y. Zheng e HC. Pant, Squid (Loligo pealei) giant fiber system: a model for studying neurodegeneration and dementia?, in Biol Bull, vol. 210, n. 3, giugno 2006, pp. 318-33, PMID 16801505.
- ^ RR. Llinás, M. Sugimori, KA. Moran, JE. Moreira e M. Fukuda, Vesicular reuptake inhibition by a synaptotagmin I C2B domain antibody at the squid giant synapse., in Proc Natl Acad Sci U S A, vol. 101, n. 51, dicembre 2004, pp. 17855-60, DOI:10.1073/pnas.0408200101, PMID 15591349.
- ^ GD. Beaven, PT. Erskine, JN. Wright, F. Mohammed, R. Gill, SP. Wood, J. Vernon, KP. Giese e JB. Cooper, Crystallization and preliminary X-ray diffraction analysis of calexcitin from Loligo pealei: a neuronal protein implicated in learning and memory., in Acta Crystallogr Sect F Struct Biol Cryst Commun, vol. 61, Pt 10, ottobre 2005, pp. 879-81, DOI:10.1107/S1744309105026758, PMID 16511184.
- ^ M. Guida, M. Guida, B. De Felice, D. Santafede, R. D'Alessandro, A. Di Spiezio Sardo, M. Scognamiglio, C. Ferrara e G. Bifulco, Assessment of DNA damage by RAPD in Paracentrotus lividus embryos exposed to amniotic fluid from residents living close to waste landfill sites., in J Biomed Biotechnol, vol. 2010, 2010, DOI:10.1155/2010/251767, PMID 20706694.
- ^ M. Agnello, G. Morici e AM. Rinaldi, A method for measuring mitochondrial mass and activity., in Cytotechnology, vol. 56, n. 3, marzo 2008, pp. 145-9, DOI:10.1007/s10616-008-9143-2, PMID 19002852.
- ^ S. Ravera, C. Falugi, D. Calzia, IM. Pepe, I. Panfoli e A. Morelli, First cell cycles of sea urchin Paracentrotus lividus are dramatically impaired by exposure to extremely low-frequency electromagnetic field., in Biol Reprod, vol. 75, n. 6, dicembre 2006, pp. 948-53, DOI:10.1095/biolreprod.106.051227, PMID 16957026.
- ^ N. Borchert, C. Dieterich, K. Krug, W. Schütz, S. Jung, A. Nordheim, RJ. Sommer e B. Macek, Proteogenomics of Pristionchus pacificus reveals distinct proteome structure of nematode models., in Genome Res, vol. 20, n. 6, giugno 2010, pp. 837-46, DOI:10.1101/gr.103119.109, PMID 20237107.
- ^ E. de Wit, SE. Linsen, E. Cuppen e E. Berezikov, Repertoire and evolution of miRNA genes in four divergent nematode species., in Genome Res, vol. 19, n. 11, novembre 2009, pp. 2064-74, DOI:10.1101/gr.093781.109, PMID 19755563.
- ^ A. Click, CH. Savaliya, S. Kienle, M. Herrmann e A. Pires-daSilva, Natural variation of outcrossing in the hermaphroditic nematode Pristionchus pacificus., in BMC Evol Biol, vol. 9, 2009, p. 75, DOI:10.1186/1471-2148-9-75, PMID 19379507.
- ^ LS. Tang, ML. Goeritz, JS. Caplan, AL. Taylor, M. Fisek e E. Marder, Precise temperature compensation of phase in a rhythmic motor pattern., in PLoS Biol, vol. 8, n. 8, 2010, DOI:10.1371/journal.pbio.1000469, PMID 20824168.
- ^ ND. DeLong e MP. Nusbaum, Hormonal modulation of sensorimotor integration., in J Neurosci, vol. 30, n. 7, febbraio 2010, pp. 2418-27, DOI:10.1523/JNEUROSCI.5533-09.2010, PMID 20164325.
- ^ AI. Selverston, A. Szücs, R. Huerta, R. Pinto e M. Reyes, Neural mechanisms underlying the generation of the lobster gastric mill motor pattern., in Front Neural Circuits, vol. 3, 2009, p. 12, DOI:10.3389/neuro.04.012.2009, PMID 19893763.
- ^ JM. Goaillard, AL. Taylor, DJ. Schulz e E. Marder, Functional consequences of animal-to-animal variation in circuit parameters., in Nat Neurosci, vol. 12, n. 11, novembre 2009, pp. 1424-30, DOI:10.1038/nn.2404, PMID 19838180.
- ^ D. Dreyer, H. Vitt, S. Dippel, B. Goetz, B. El Jundi, M. Kollmann, W. Huetteroth e J. Schachtner, 3D Standard Brain of the Red Flour Beetle Tribolium Castaneum: A Tool to Study Metamorphic Development and Adult Plasticity., in Front Syst Neurosci, vol. 4, 2010, p. 3, DOI:10.3389/neuro.06.003.2010, PMID 20339482.
- ^ AD. Peel, Forward genetics in Tribolium castaneum: opening new avenues of research in arthropod biology., in J Biol, vol. 8, n. 12, 2009, p. 106, DOI:10.1186/jbiol208, PMID 20053302.
- ^ HS. Kim, T. Murphy, J. Xia, D. Caragea, Y. Park, RW. Beeman, MD. Lorenzen, S. Butcher e JR. Manak, BeetleBase in 2010: revisions to provide comprehensive genomic information for Tribolium castaneum., in Nucleic Acids Res, vol. 38, Database issue, gennaio 2010, pp. D437-42, DOI:10.1093/nar/gkp807, PMID 19820115.
- ^ TD. Kocher, WR. Jeffery, DM. Parichy, CL. Peichel, JT. Streelman e GH. Thorgaard, Special feature--roundtable discussion. Fish models for studying adaptive evolution and speciation., in Zebrafish, vol. 2, n. 3, 2005, pp. 147-56, DOI:10.1089/zeb.2005.2.147, PMID 18248189.
- ^ J. Bradbury, Small fish, big science., in PLoS Biol, vol. 2, n. 5, maggio 2004, pp. E148, DOI:10.1371/journal.pbio.0020148, PMID 15138510.
- ^ AJ. Hill, H. Teraoka, W. Heideman e RE. Peterson, Zebrafish as a model vertebrate for investigating chemical toxicity., in Toxicol Sci, vol. 86, n. 1, luglio 2005, pp. 6-19, DOI:10.1093/toxsci/kfi110, PMID 15703261.
- ^ JM. Spitsbergen e ML. Kent, The state of the art of the zebrafish model for toxicology and toxicologic pathology research--advantages and current limitations., in Toxicol Pathol, 31 Suppl, pp. 62-87, PMID 12597434.
- ^ (EN) www.official-documents.gov.uk (PDF), su official-documents.gov.uk.
- ^ (EN) Animal-Testing Ban for Cosmetics to Be Upheld, EU Court Rules - Bloomberg, su bloomberg.com.
- ^ (EN) US FDA/CFSAN - Animal Testing, su cfsan.fda.gov (archiviato dall'url originale il 23 maggio 2007).
- ^ Safar P, Behringer W, Böttiger BW, Sterz F, Cerebral resuscitation potentials for cardiac arrest, in Crit. Care Med., vol. 30, 4 Suppl, aprile 2002, pp. S140–4, PMID 11940789.
- ^ Suckow, Mark A.; Terril, Lizabeth A.; Clemons, Donna J., The laboratory guinea pig, Boca Raton, CRC Press, 1998, ISBN 0-8493-2564-1.
- ^ AL. Poirrier, P. Van den Ackerveken, TS. Kim, R. Vandenbosch, L. Nguyen, PP. Lefebvre e B. Malgrange, Ototoxic drugs: difference in sensitivity between mice and guinea pigs., in Toxicol Lett, vol. 193, n. 1, marzo 2010, pp. 41-9, DOI:10.1016/j.toxlet.2009.12.003, PMID 20015469.
- ^ P. Schwarz, P. Strnad, N. Singer, F. Oswald, R. Ehehalt, G. Adler e H. Kulaksiz, Identification, sequencing, and cellular localization of hepcidin in guinea pig (Cavia porcellus)., in J Endocrinol, vol. 202, n. 3, settembre 2009, pp. 389-96, DOI:10.1677/JOE-09-0191, PMID 19553281.
- ^ a b R. Dumke, I. Catrein, R. Herrmann e E. Jacobs, Preference, adaptation and survival of Mycoplasma pneumoniae subtypes in an animal model., in Int J Med Microbiol, vol. 294, n. 2-3, settembre 2004, pp. 149-55, PMID 15493825.
- ^ R. O'Toole, Experimental models used to study human tuberculosis., in Adv Appl Microbiol, vol. 71, 2010, pp. 75-89, DOI:10.1016/S0065-2164(10)71003-0, PMID 20378051.
- ^ M. Möller, E. de Wit e EG. Hoal, Past, present and future directions in human genetic susceptibility to tuberculosis., in FEMS Immunol Med Microbiol, vol. 58, n. 1, febbraio 2010, pp. 3-26, DOI:10.1111/j.1574-695X.2009.00600.x, PMID 19780822.
- ^ A. Rawat, KA. Gust, MO. Elasri e EJ. Perkins, Quail Genomics: a knowledgebase for Northern bobwhite., in BMC Bioinformatics, 11 Suppl 6, 2010, pp. S13, DOI:10.1186/1471-2105-11-S6-S13, PMID 20946596.
- ^ A. Biswas, OS. Ranganatha e J. Mohan, The effect of different foam concentrations on sperm motility in Japanese quail., in Vet Med Int, vol. 2010, 2010, p. 564921, DOI:10.4061/2010/564921, PMID 21076546.
- ^ Patricia Pope Bartlett e Michele Earle-Bridges, The hamster handbook, Hauppauge, NY, Barron's, 2003, ISBN 978-0-7641-2294-1.
- ^ DA. Haake, Hamster model of leptospirosis., in Curr Protoc Microbiol, Chapter 12, settembre 2006, pp. Unit 12E.2, DOI:10.1002/9780471729259.mc12e02s02, PMID 18770576.
- ^ A. Lee, Animal models and vaccine development., in Baillieres Clin Gastroenterol, vol. 9, n. 3, settembre 1995, pp. 615-32, PMID 8563056.
- ^ MA. Meredith e BE. Stein, Visual, auditory, and somatosensory convergence on cells in superior colliculus results in multisensory integration., in J Neurophysiol, vol. 56, n. 3, settembre 1986, pp. 640-62, PMID 3537225.
- ^ BR. Møller e PA. Mårdh, Animal models for the study of Chlamydial infections of the urogenital tract., in Scand J Infect Dis Suppl, vol. 32, 1982, pp. 103-8, PMID 6813962.
- ^ YS. Rao, ZF. Wang, XW. Chai, GZ. Wu, M. Zhou, QH. Nie e XQ. Zhang, Selection for the compactness of highly expressed genes in Gallus gallus., in Biol Direct, vol. 5, 2010, p. 35, DOI:10.1186/1745-6150-5-35, PMID 20465857.
- ^ a b WC. Warren, DF. Clayton, H. Ellegren, AP. Arnold, LW. Hillier, A. Künstner, S. Searle, S. White e AJ. Vilella, The genome of a songbird., in Nature, vol. 464, n. 7289, aprile 2010, pp. 757-62, DOI:10.1038/nature08819, PMID 20360741.
- ^ H. Ono, N. Nakao, T. Yamamura, K. Kinoshita, M. Mizutani, T. Namikawa, M. Iigo, S. Ebihara e T. Yoshimura, Red jungle fowl (Gallus gallus) as a model for studying the molecular mechanism of seasonal reproduction., in Anim Sci J, vol. 80, n. 3, giugno 2009, pp. 328-32, DOI:10.1111/j.1740-0929.2009.00628.x, PMID 20163644.
- ^ DI. Shushevich, AI. Fomenko e AG. Khalmuradov, , in Biokhimiia, vol. 42, n. 2, febbraio 1977, pp. 251-6, PMID 192347.
- ^ Wolfe, Linda D.; Fuentes, Agustin, Primates face to face: conservation implications of human-nonhuman primate interconnections, Cambridge, UK, Cambridge University Press, 2002, ISBN 0-521-79109-X.
- ^ KF. Snowden, ES. Didier, JM. Orenstein e JA. Shadduck, Animal models of human microsporidial infections., in Lab Anim Sci, vol. 48, n. 6, dicembre 1998, pp. 589-92, PMID 10090081.
- ^ AP. Sripati e CR. Olson, Global image dissimilarity in macaque inferotemporal cortex predicts human visual search efficiency., in J Neurosci, vol. 30, n. 4, gennaio 2010, pp. 1258-69, DOI:10.1523/JNEUROSCI.1908-09.2010, PMID 20107054.
- ^ JM. Samonds, BR. Potetz e TS. Lee, Cooperative and competitive interactions facilitate stereo computations in macaque primary visual cortex., in J Neurosci, vol. 29, n. 50, dicembre 2009, pp. 15780-95, DOI:10.1523/JNEUROSCI.2305-09.2009, PMID 20016094.
- ^ T. Nekovarova, J. Nedvidek, D. Klement e J. Bures, Spatial decisions and cognitive strategies of monkeys and humans based on abstract spatial stimuli in rotation test., in Proc Natl Acad Sci U S A, vol. 106, n. 36, settembre 2009, pp. 15478-82, DOI:10.1073/pnas.0907053106, PMID 19706408.
- ^ I. Adachi, DP. Chou e RR. Hampton, Thatcher effect in monkeys demonstrates conservation of face perception across primates., in Curr Biol, vol. 19, n. 15, agosto 2009, pp. 1270-3, DOI:10.1016/j.cub.2009.05.067, PMID 19559613.
- ^ NA. Wilson e DI. Watkins, Is an HIV vaccine possible?, in Braz J Infect Dis, vol. 13, n. 4, agosto 2009, pp. 304-10, PMID 20231996.
- ^ G. Silvestri, Immunity in natural SIV infections., in J Intern Med, vol. 265, n. 1, gennaio 2009, pp. 97-109, DOI:10.1111/j.1365-2796.2008.02049.x, PMID 19093963.
- ^ G. Grimaldi Jr, The utility of rhesus monkey (Macaca mulatta) and other non-human primate models for preclinical testing of Leishmania candidate vaccines., in Mem Inst Oswaldo Cruz, vol. 103, n. 7, novembre 2008, pp. 629-44, PMID 19057811.
- ^ KV. Anderson e PW. Ingham, The transformation of the model organism: a decade of developmental genetics., in Nat Genet, 33 Suppl, marzo 2003, pp. 285-93, DOI:10.1038/ng1105, PMID 12610538.
- ^ a b T. Sasado, M. Tanaka, K. Kobayashi, T. Sato, M. Sakaizumi e K. Naruse, The National BioResource Project Medaka (NBRP Medaka): an integrated bioresource for biological and biomedical sciences., in Exp Anim, vol. 59, n. 1, 2010, pp. 13-23, PMID 20224166.
- ^ JM. Fortier e TA. Graubert, Murine models of human acute myeloid leukemia., in Cancer Treat Res, vol. 145, 2010, pp. 183-96, DOI:10.1007/978-0-387-69259-3_11, PMID 20306252.
- ^ B. Zhang, Z. Duan e Y. Zhao, Mouse models with human immunity and their application in biomedical research., in J Cell Mol Med, vol. 13, n. 6, giugno 2009, pp. 1043-58, DOI:10.1111/j.1582-4934.2008.00347.x, PMID 18419795.
- ^ DR. Reed, X. Li, AH. McDaniel, K. Lu, S. Li, MG. Tordoff, RA. Price e AA. Bachmanov, Loci on chromosomes 2, 4, 9, and 16 for body weight, body length, and adiposity identified in a genome scan of an F2 intercross between the 129P3/J and C57BL/6ByJ mouse strains., in Mamm Genome, vol. 14, n. 5, maggio 2003, pp. 302-13, PMID 12856282.
- ^ GL. Wolff e P. Whittaker, Dose-response effects of ectopic agouti protein on iron overload and age-associated aspects of the Avy/a obese mouse phenome., in Peptides, vol. 26, n. 10, ottobre 2005, pp. 1697-711, DOI:10.1016/j.peptides.2004.12.033, PMID 15982784.
- ^ L. Ding, WW. Kuhne, DE. Hinton, J. Song e WS. Dynan, Quantifiable biomarkers of normal aging in the Japanese medaka fish (Oryzias latipes)., in PLoS One, vol. 5, n. 10, 2010, pp. e13287, DOI:10.1371/journal.pone.0013287, PMID 20949019.
- ^ A. Shima e A. Shimada, The Japanese medaka, Oryzias latipes, as a new model organism for studying environmental germ-cell mutagenesis., in Environ Health Perspect, 102 Suppl 12, dicembre 1994, pp. 33-5, PMID 7713031.
- ^ NY. Ho, VW. Li, WL. Poon e SH. Cheng, Cloning and developmental expression of kinesin superfamily7 (kif7) in the brackish medaka (Oryzias melastigma), a close relative of the Japanese medaka (Oryzias latipes)., in Mar Pollut Bull, vol. 57, n. 6-12, 2008, pp. 425-32, DOI:10.1016/j.marpolbul.2008.02.044, PMID 18423496.
- ^ IL. Iessi, A. Bueno, YK. Sinzato, KN. Taylor, MV. Rudge e DC. Damasceno, Evaluation of neonatally-induced mild diabetes in rats: Maternal and fetal repercussions., in Diabetol Metab Syndr, vol. 2, n. 1, 2010, p. 37, DOI:10.1186/1758-5996-2-37, PMID 20529353.
- ^ MR. Dwinell, EA. Worthey, M. Shimoyama, B. Bakir-Gungor, J. DePons, S. Laulederkind, T. Lowry, R. Nigram e V. Petri, The Rat Genome Database 2009: variation, ontologies and pathways., in Nucleic Acids Res, vol. 37, Database issue, gennaio 2009, pp. D744-9, DOI:10.1093/nar/gkn842, PMID 18996890.
- ^ J. Sedý, J. Zicha, J. Kunes, P. Jendelová e E. Syková, Rapid but not slow spinal cord compression elicits neurogenic pulmonary edema in the rat., in Physiol Res, vol. 58, n. 2, 2009, pp. 269-77, PMID 18380532.
- ^ SM. Cohen, LL. Arnold, M. Eldan, AS. Lewis e BD. Beck, Methylated arsenicals: the implications of metabolism and carcinogenicity studies in rodents to human risk assessment., in Crit Rev Toxicol, vol. 36, n. 2, febbraio 2006, pp. 99-133, PMID 16736939.
- ^ L. Shaughnessy, B. Chamblin, L. McMahon, A. Nair, MB. Thomas, J. Wakefield, F. Koentgen e R. Ramabhadran, Novel approaches to models of Alzheimer's disease pathology for drug screening and development., in J Mol Neurosci, vol. 24, n. 1, 2004, pp. 23-32, DOI:10.1385/JMN:24:1:023, PMID 15314246.
- ^ Don W. Wilson e Deeann Reeder, Mammal species of the world: a taxonomic and geographic reference, Baltimore, Johns Hopkins University Press, 2005, ISBN 978-0-8018-8221-0.
- ^ L. Nanassy, J. Griffin, BR. Emery e DT. Carrell, The marmoset and cotton rat as animal models for the study of sperm chromatin packaging., in Syst Biol Reprod Med, vol. 56, n. 3, giugno 2010, pp. 207-12, DOI:10.3109/19396361003653311, PMID 20536320.
- ^ K. Chen, T. Baxter, WM. Muir, MA. Groenen e LB. Schook, Genetic resources, genome mapping and evolutionary genomics of the pig (Sus scrofa)., in Int J Biol Sci, vol. 3, n. 3, 2007, pp. 153-65, PMID 17384734.
- ^ AL. Ferraz, A. Ojeda, M. López-Béjar, LT. Fernandes, A. Castelló, JM. Folch e M. Pérez-Enciso, Transcriptome architecture across tissues in the pig., in BMC Genomics, vol. 9, 2008, p. 173, DOI:10.1186/1471-2164-9-173, PMID 18416811.
- ^ AM. Reddy, Y. Zheng, G. Jagadeeswaran, SL. Macmil, WB. Graham, BA. Roe, U. Desilva, W. Zhang e R. Sunkar, Cloning, characterization and expression analysis of porcine microRNAs., in BMC Genomics, vol. 10, 2009, p. 65, DOI:10.1186/1471-2164-10-65, PMID 19196471.
- ^ B. Gesslein, G. Håkansson, R. Carpio, L. Gustafsson, MT. Perez e M. Malmsjö, Mitogen-activated protein kinases in the porcine retinal arteries and neuroretina following retinal ischemia-reperfusion., in Mol Vis, vol. 16, 2010, pp. 392-407, PMID 20300568.
- ^ J. Guduric-Fuchs, LJ. Ringland, P. Gu, M. Dellett, DB. Archer e T. Cogliati, Immunohistochemical study of pig retinal development., in Mol Vis, vol. 15, 2009, pp. 1915-28, PMID 19784390.
- ^ IK. Petropoulos, JA. Pournaras, AN. Stangos e CJ. Pournaras, Effect of systemic nitric oxide synthase inhibition on optic disc oxygen partial pressure in normoxia and in hypercapnia., in Invest Ophthalmol Vis Sci, vol. 50, n. 1, gennaio 2009, pp. 378-84, DOI:10.1167/iovs.08-2413, PMID 18676634.
- ^ F. Fallarino, G. Luca, M. Calvitti, F. Mancuso, C. Nastruzzi, MC. Fioretti, U. Grohmann, E. Becchetti e A. Burgevin, Therapy of experimental type 1 diabetes by isolated Sertoli cell xenografts alone., in J Exp Med, vol. 206, n. 11, ottobre 2009, pp. 2511-26, DOI:10.1084/jem.20090134, PMID 19822646.
- ^ K. Gelse, C. Mühle, O. Franke, J. Park, M. Jehle, K. Durst, M. Göken, F. Hennig e K. von der Mark, Cell-based resurfacing of large cartilage defects: long-term evaluation of grafts from autologous transgene-activated periosteal cells in a porcine model of osteoarthritis., in Arthritis Rheum, vol. 58, n. 2, febbraio 2008, pp. 475-88, DOI:10.1002/art.23124, PMID 18240212.
- ^ X. Zhang, J. Li, XY. Liu, YL. Sun, CM. Zhang e SL. Wang, Morphological characteristics of submandibular glands of miniature pig., in Chin Med J (Engl), vol. 118, n. 16, agosto 2005, pp. 1368-73, PMID 16157032.
- ^ CM. Benskin, G. Rhodes, RW. Pickup, K. Wilson e IR. Hartley, Diversity and temporal stability of bacterial communities in a model passerine bird, the zebra finch., in Mol Ecol, novembre 2010, DOI:10.1111/j.1365-294X.2010.04892.x, PMID 21054607.
- ^ M. Luo, Y. Yu, H. Kim, D. Kudrna, Y. Itoh, RJ. Agate, E. Melamed, JL. Goicoechea e J. Talag, Utilization of a zebra finch BAC library to determine the structure of an avian androgen receptor genomic region., in Genomics, vol. 87, n. 1, gennaio 2006, pp. 181-90, DOI:10.1016/j.ygeno.2005.09.005, PMID 16321505.
- ^ Y. Yamanoue, M. Miya, K. Matsuura, S. Miyazawa, N. Tsukamoto, H. Doi, H. Takahashi, K. Mabuchi e M. Nishida, Explosive speciation of Takifugu: another use of fugu as a model system for evolutionary biology., in Mol Biol Evol, vol. 26, n. 3, marzo 2009, pp. 623-9, DOI:10.1093/molbev/msn283, PMID 19074759.
- ^ YH. Loh, S. Brenner e B. Venkatesh, Investigation of loss and gain of introns in the compact genomes of pufferfishes (Fugu and Tetraodon)., in Mol Biol Evol, vol. 25, n. 3, marzo 2008, pp. 526-35, DOI:10.1093/molbev/msm278, PMID 18089580.
- ^ S. Imai, T. Sasaki, A. Shimizu, S. Asakawa, H. Hori e N. Shimizu, The genome size evolution of medaka (Oryzias latipes) and fugu (Takifugu rubripes)., in Genes Genet Syst, vol. 82, n. 2, aprile 2007, pp. 135-44, PMID 17507779.
- ^ V. Veeramachaneni e W. Makalowski, DED: Database of Evolutionary Distances., in Nucleic Acids Res, vol. 33, Database issue, gennaio 2005, pp. D442-6, DOI:10.1093/nar/gki094, PMID 15608234.
- ^ EJ. Pearl, CK. Bilogan, S. Mukhi, DD. Brown e ME. Horb, Xenopus pancreas development., in Dev Dyn, vol. 238, n. 6, giugno 2009, pp. 1271-86, DOI:10.1002/dvdy.21935, PMID 19334283.
- ^ E. Segerdell, JB. Bowes, N. Pollet e PD. Vize, An ontology for Xenopus anatomy and development., in BMC Dev Biol, vol. 8, 2008, p. 92, DOI:10.1186/1471-213X-8-92, PMID 18817563.
- ^ DA. Yergeau e PE. Mead, Manipulating the Xenopus genome with transposable elements., in Genome Biol, 8 Suppl 1, 2007, pp. S11, DOI:10.1186/gb-2007-8-s1-s11, PMID 18047688.
- ^ JB. Bowes, KA. Snyder, E. Segerdell, R. Gibb, C. Jarabek, E. Noumen, N. Pollet e PD. Vize, Xenbase: a Xenopus biology and genomics resource., in Nucleic Acids Res, vol. 36, Database issue, gennaio 2008, pp. D761-7, DOI:10.1093/nar/gkm826, PMID 17984085.
- ^ ML. Tomlinson, RA. Field e GN. Wheeler, Xenopus as a model organism in developmental chemical genetic screens., in Mol Biosyst, vol. 1, n. 3, settembre 2005, pp. 223-8, DOI:10.1039/b506103b, PMID 16880986.
- ^ G. Kreil, Antimicrobial peptides from amphibian skin: an overview., in Ciba Found Symp, vol. 186, 1994, pp. 77-85; discussion 85-90, PMID 7768159.
- ^ I. Keller, IC. Chintauan-Marquier, P. Veltsos e RA. Nichols, Ribosomal DNA in the grasshopper Podisma pedestris: escape from concerted evolution., in Genetics, vol. 174, n. 2, ottobre 2006, pp. 863-74, DOI:10.1534/genetics.106.061341, PMID 16951064.
- ^ F. Ishikawa, , in Shikai Tenbo, vol. 63, n. 7, giugno 1984, pp. 1419-29, PMID 6593840.
- ^ ML. Arnold, R. Appels e DD. Shaw, The heterochromatin of grasshoppers from the Caledia captiva species complex. I. Sequence evolution and conservation in a highly repeated DNA family., in Mol Biol Evol, vol. 3, n. 1, gennaio 1986, pp. 29-43, PMID 3444395.
- ^ R. Tollrian e F. Leese, Ecological genomics: steps towards unraveling the genetic basis of inducible defenses in Daphnia., in BMC Biol, vol. 8, 2010, p. 51, DOI:10.1186/1741-7007-8-51, PMID 20529235.
- ^ Florian Odronitz, Sebastian Becker & Martin Kollmar, Reconstructing the phylogeny of 21 completely sequenced arthropod species based on their motor proteins, in BMC Genomics, vol. 10, 2009, p. 173, DOI:10.1186/1471-2164-10-173.
- ^ JGI-Led Team Sequences Frog Genome, in GenomeWeb.com, Genome Web, 29 aprile 2010. URL consultato il 30 aprile 2010 (archiviato dall'url originale il 7 agosto 2011).
Bibliografia
- Spitsbergen J.M. and Kent M.L. (2003). The state of the art of the zebrafish model for toxicology and toxicologic pathology research—advantages and current limitations. Toxicol Pathol. 31 (Supplement), 62-87. PubMed Abstract Link => PMID 12597434.Testo su Zebrafish disponibile gratuitamente[collegamento interrotto].
- (EN) Riddle, Donald L.; Blumenthal, Thomas; Meyer, Barbara J.; and Priess, James R. (Eds.). (1997). C. ELEGANS II. Woodbury, NY: Cold Spring Harbor Press. ISBN 0-87969-532-3. Testo su C.elegans disponibile gratuitamente.
- (EN) Hoekstra, Merl F.; Nickoloff, Jac A., DNA damage and repair, Totowa, NJ, Humana Press, 1998, ISBN 0-89603-356-2.
- (EN) H. Jane Brockmann, Timothy J. Roper e Marc Naguib, Advances in the Study of Behavior, Academic Press, 19 agosto 2008, pp. 502–, ISBN 978-0-12-004538-9. URL consultato il 21 novembre 2010.
- (EN) Zann, Richard A., The zebra finch: a synthesis of field and laboratory studies, Oxford , Oxford University Press, 1996, ISBN 0-19-854079-5.
- (EN) Don W. Wilson e Deeann Reeder, Mammal species of the world: a taxonomic and geographic reference, Baltimore, Johns Hopkins University Press, 2005, ISBN 978-0-8018-8221-0.
- (EN) Patricia Pope Bartlett e Michele Earle-Bridges, The hamster handbook, Hauppauge, NY, Barron's, 2003, ISBN 978-0-7641-2294-1.
- (EN) Wolfe, Linda D.; Fuentes, Agustin, Primates face to face: conservation implications of human-nonhuman primate interconnections, Cambridge, UK, Cambridge University Press, 2002, ISBN 0-521-79109-X.
- (EN) Schilthuizen, Menno, Frogs, flies, and dandelions: speciation--the evolution of new species, Oxford , Oxford University Press, 2001, ISBN 0-19-850393-8.
- (EN) Winfried Lampert & Ulrich Sommer, Predation, in Limnoecology: The Ecology of Lakes and Streams, 2nd, Oxford University Press, 2007, pp. 162–179, ISBN 978-0-19-921393-1.
Voci correlate
Altri progetti
 Wikimedia Commons contiene immagini o altri file su organismo modello
Wikimedia Commons contiene immagini o altri file su organismo modello
Collegamenti esterni
- (EN) Banca dati contenente i genomi di tutti gli organismi sequenziati, su ensembl.org.
- (EN) Banca dati NCBI contenente informazioni riguardanti tutti gli organismi modello, su ncbi.nlm.nih.gov.
- (EN) Altra banca dati contenente informazioni su vari organismi modello, su ceolas.org.
- (EN) Wellcome Trust description of model organisms, su wellcome.ac.uk. URL consultato il 20 novembre 2010 (archiviato dall'url originale il 5 marzo 2006).
- (EN) Model organisms in developmental biology, su developmentalbiology.de. URL consultato il 20 novembre 2010 (archiviato dall'url originale il 6 maggio 2008).
- (EN) Ludwig-Maximillians-Universität Department Biologie II, su biologie.uni-muenchen.de. URL consultato il 20 novembre 2010 (archiviato dall'url originale il 29 settembre 2007).
- (EN) Zebrafish GenomeWiki Community Annotation Project mantenuto dall'Institute of Genomics and Integrative Biology
- (EN) Workhorse Zoo by Adam Zaretsky, su emutagen.com. URL consultato il 20 novembre 2010 (archiviato dall'url originale il 10 febbraio 2015).